 打印
打印
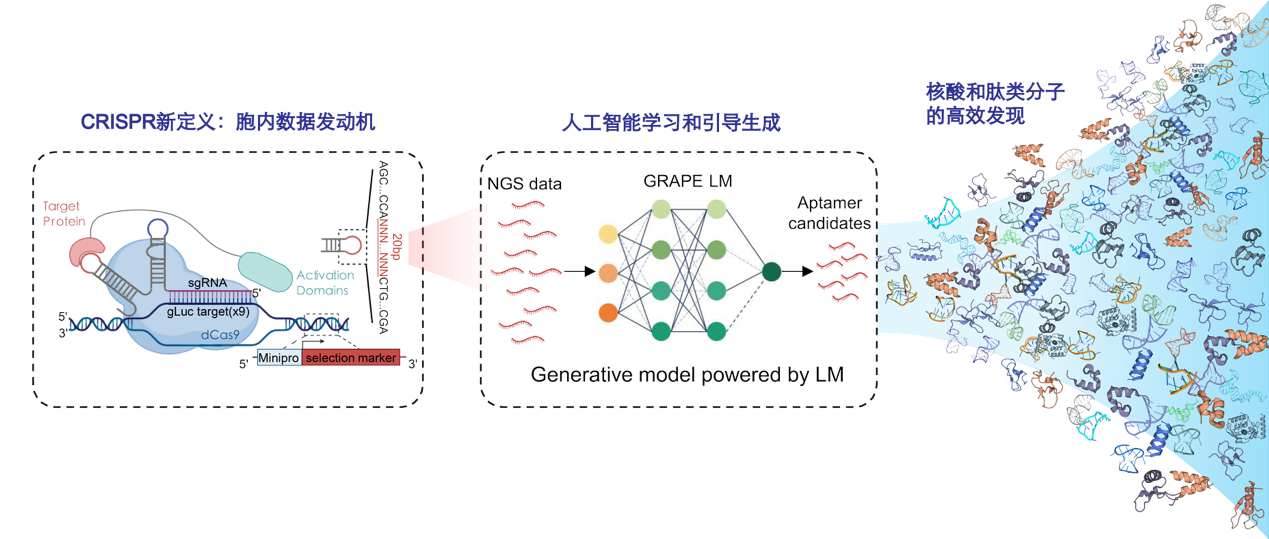
图 生物分子药物发掘的新技术路线
在国家自然科学基金项目(批准号:91957121、82273967、82273890)等资助下,中国科学院深圳先进技术研究院王宇研究员团队联合深圳大学人工智能学院张军团队和天津大学药学院张阳教授团队在生物分子药物发掘技术方面取得进展,相关成果以“由GRAPE-LM辅助的单轮RNA适配体进化(Single round evolution of RNA aptamers with GRAPE-LM)”为题,于2026年2月6日在《自然·生物技术》(Nature Biotechnology)杂志在线发表,并被编辑团队选为亮点论文,邀请作者发表研究简报(Research Briefing)介绍论文成果和研究历程。论文和简报链接:https://www.nature.com/articles/s41587-026-03007-5;https://www.nature.com/articles/s41587-026-03008-4
核酸适配体(aptamer)是一类短的单链DNA(ssDNA)或RNA寡核苷酸,能够折叠形成特定三维结构,并以“结构分子”的方式高亲和力结合蛋白或小分子,从而具备开发成为核酸药物和诊断探针的潜力。目前,RNA适配体药物已有两种获批上市。然而,适配体发现长期依赖指数富集的配体系统进化技术(SELEX),通常需要多轮、强人工参与的筛选与优化;同时,在体外简化条件下获得的适配体,亲和力和特异性常常有限,限制了其开发成核酸药物和探针的潜力。
研究团队在既往工作中以CRISPR基因编辑系统为生物分子支架,赋予它胞内高保真RNA数据发动机的新定义。团队前期研发了CRISmers(CRISPR/Cas based aptamers screening system)体系,适配体筛选从溶液和细胞表面体系推进到细胞内环境,使筛选过程天然包含内源生物学机制,从源头提升生物学相关性。在最新工作中,研究团队进一步提出GRAPE-LM人工智能架构(Generator of RNA Aptamers Powered by activity-guided Evolution and Language Model),将“胞内筛选数据”与“核酸语言模型”耦合为一条端到端的一轮式高效进化路径:模型以自注意力神经网络(Transformer)条件自编码器为骨架,融合核酸语言模型,并由CRISmers在胞内环境产生的筛选数据提供“活性引导”,实现RNA适配体的一轮进化与生成。GRAPE-LM将“实验进化”从传统的多轮循环,重构为“物理进化 + 数字优化”的两阶段。高质量数据和高性能AI强强联合,在三类靶标上,仅用1轮即可获得优于既往SELEX 6–16轮所得到的适配体的先导序列。此外,通过预研,研究团队已证实该技术路线可成功拓展至肽类分子,这表明其具备向多类生物分子横向迁移的潜力,通用性得到进一步拓宽(图)。
该研究提出了加速生物分子进化和候选药物发掘的新范式,为生物分子药物的开发提供了新的技术路线。
