香港浸会大学蔡宗苇团队与夏亦荠团队在《自然-实验手册》发表NAD tagSeq新方法用于分析带有NAD“帽子”的RNA
近日,香港浸会大学环境与生物分析国家重点实验室蔡宗苇教授与夏亦荠团队开发了一种名为NAD tagSeq的新方法以用于鉴定和分析戴有NAD“帽子”的RNA。RNA的两端具有各种修饰,而这些修饰又被形象地称为RNA的“帽子”和“尾巴”。早前的研究就发现,真核生物的信使RNA上普遍带有N7-甲基鸟苷(m7G)结构的“帽子”。此后,一些研究发现,原核和真核生物会将烟酰胺腺嘌呤二核苷酸分子(NAD)当作转录的起始材料整合到RNA的5‘端。这种RNA的5‘端修饰又被称为NAD“帽子”或5’端帽,而带有NAD“帽子”的RNA则被称作NAD-RNA。NAD“帽子”在原核和真核生物体中的广泛存在,表明其有可能参与基因的调控。
研究团队最近开发了一种名为NAD tagSeq的方法,将NAD-RNA标记上一个合成的RNA,然后通过牛津纳米孔测序技术实现对RNA的直接测序。该方法借鉴了NAD caputreSeq的思路。NAD captureSeq首先通过ADPRC酶催化的炔基化反应,将NAD分子上的烟酰胺基团替换为炔基基团,然后通过铜离子催化的炔基-叠氮环化加成反应(CuAAC反应)将NAD-RNA标记上生物素。NAD tagSeq也使用了这两步反应,但在CuAAC反应中将生物素替换为合成的RNA,从而将该合成的RNA直接连接在NAD-RNA上作为标记。该RNA标记可以通过牛津纳米孔测序技术直接进行测序,从而指示NAD-RNA的存在(详见图1)。
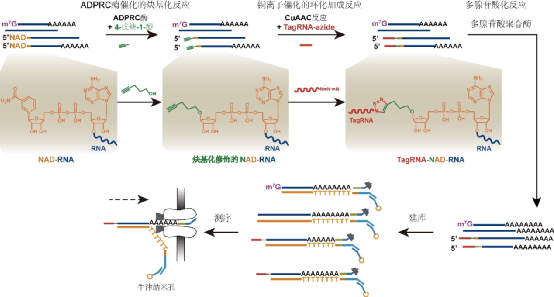
图 1NAD tagSeq的实验设计。
首先,NAD“帽子”在ADPRC酶催化下连接上炔基基团。然后,通过CuAAC反应(铜离子催化的炔基-叠氮环化加成反应)在炔基化的NAD-RNA的5‘端连上叠氮化的标记RNA(tagRNA-azide)。因为牛津纳米孔只能对带有多腺苷酸“尾巴”的RNA进行测序,所以如果NAD-RNA没有该“尾巴”,需要通过多腺苷酸化反应将其连上该“尾巴”。最后,这些标记的NAD-RNA和其他RNA就可一起通过牛津纳米孔技术进行直接测序。
NAD tagSeq 提供了一种新的方法来分析戴有NAD“帽子”的RNA。标记的RNA可用于区分NAD-RNA和其他RNA。NAD tagSeq直接进行RNA测序,因而不需要将RNA逆转录为cDNA,因而比需要逆转录的NAD captureSeq方法简单些。而且,NAD tagSeq通过RNA直接的测序,不需要将RNA碎片化为短链,可以保留长链RNA的结构,有利于进一步分析长链NAD-RNA的结构。同时,NAD tagSeq还可以实现对同一基因的转录产物中NAD-RNA和非NAD-RNA的相对丰度的分析和比较。
体外实验表明,NAD“帽子”在转录的一开始就可以被RNA聚合酶整合到RNA的5’端。这很可能也是体内NAD-RNA的主要形成途径。这表明,NAD-RNA水平直接受到体内NAD小分子的影响。而NAD分子又是人体内重要的辅酶,并受到氧化还原以及分子代谢水平的调控。相关的研究预示,体内的NAD-RNA水平不仅受到体内基因组水平的影响,还受到外界暴露组的影响。这为我们进一步研究不同环境污染物暴露情况下NAD-RNA的变化提供了事实依据和理论基础。实验室此前通过小鼠暴露环境污染物,如三氯生、PM2.5等,都可以产生严重的氧化还原的失衡,也观察到NAD小分子水平的变化。可以进一步研究这些污染物对NAD-RNA的调控情况以及后续可能的分子机理。
NAD tagSeq方法的具体实验操作发表于Nature Protocols 《自然-实验手册》中,香港浸会大学的博士生邵晓剑和张海磊为共同第一作者,蔡宗苇教授和夏亦荠教授为共同通讯作者。另外,该方法首先应用于拟南芥中NAD-RNA的鉴定,成果已发表于PNAS《美国科学院院刊》,香港浸会大学的博士生张海磊和钟欢为共同第一作者。该研究得到了中国国家自然科学基金、科技部,以及香港研究资助局、香港浸会大学研究委员会的资助。
论文链接:
